姓名分割プログラムをつくる-訂正編-
前回の記事に間違いが見つかったのでそんな感じの記事です。
間違いを直す過程でちょっと手法を見直したりしました。
前回までのおさらい
- 姓名分割プログラムを作ったよ
- 姓名分割とは、姓名の間にスペースが入っていない人名にスペースを入れることだよ(篠田麻里子→篠田 麻里子)
- 特徴量はOrderPointとLengthPointだよ
- LengthPointの計算がなんかバグってるっぽいよ
- OrderPointとLengthPointの2特徴量でロジスティック回帰をするよ
- .990の制度が出たよ
- 詳しくは前回の記事を読んでほしいよ
間違えてたところ
LengthPointの計算がなんかバグってるっぽいよ のところでした
やっぱりかよ
ただ単に計算部分のプログラムミスだったんで修正方法は割愛
間違いを直したら
まちがいを直した後にロジスティック回帰をしたところ、どちゃくそ精度が悪くなってしまいました。
回帰の方法については前回に詳しいです。
参考:前回の引用
篠田麻里子を学習用にデータ処理するとこうなります。
Name,OrderPoint,LengthPoint,Answer
篠 田麻里子,0.121212121212121,0.205,0
篠田 麻里子,0.777253191702888,0.616753480620525,1
篠田麻 里子,0.126787212337516,0.246093120543235,0
篠田麻里 子,0.10023598578629,0,0Answerは正しく区切れているかのbool
なんでだろうとおもいながらグラフを書いてみました。
横軸にOrderPoint,縦軸にLengthPoint,赤が正解の区切り位置、青が間違えた区切り位置です。
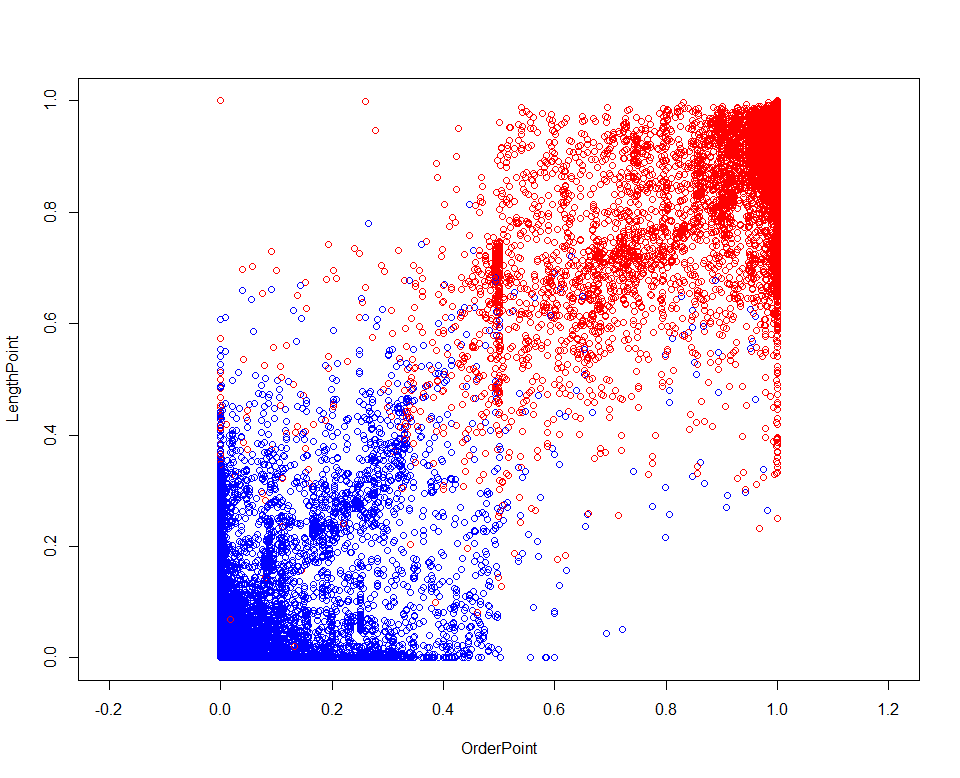
ペロ、、これは多重共線性
多重共線性とは、特徴量(説明変数)同士に相関があるときに回帰がうまくいかなくなってしまう現象です。
OrderPointの係数が5前後なのに対し、LengthPointの係数が10前後になってしまいました。
これじゃあいけませんので何かしましょう。
こういう時は主成分分析がいいという話になっているので主成分分析をしてみました。
2次元の主成分分析は感覚的にとても理解しやすいのでありがたいですね。
主成分分析(2次元)とは、分散が最大となる軸の回転方法を探す操作のことです。
この姓名分離でいうと、「右にあるのが赤で左にあるのが青!」と一番自信をもって言い切れる回転方法を探す操作のことです。
2次元で評価していたものを1次元で評価することにより、多重共線性により回帰ができなくなる問題を回避するわけです。
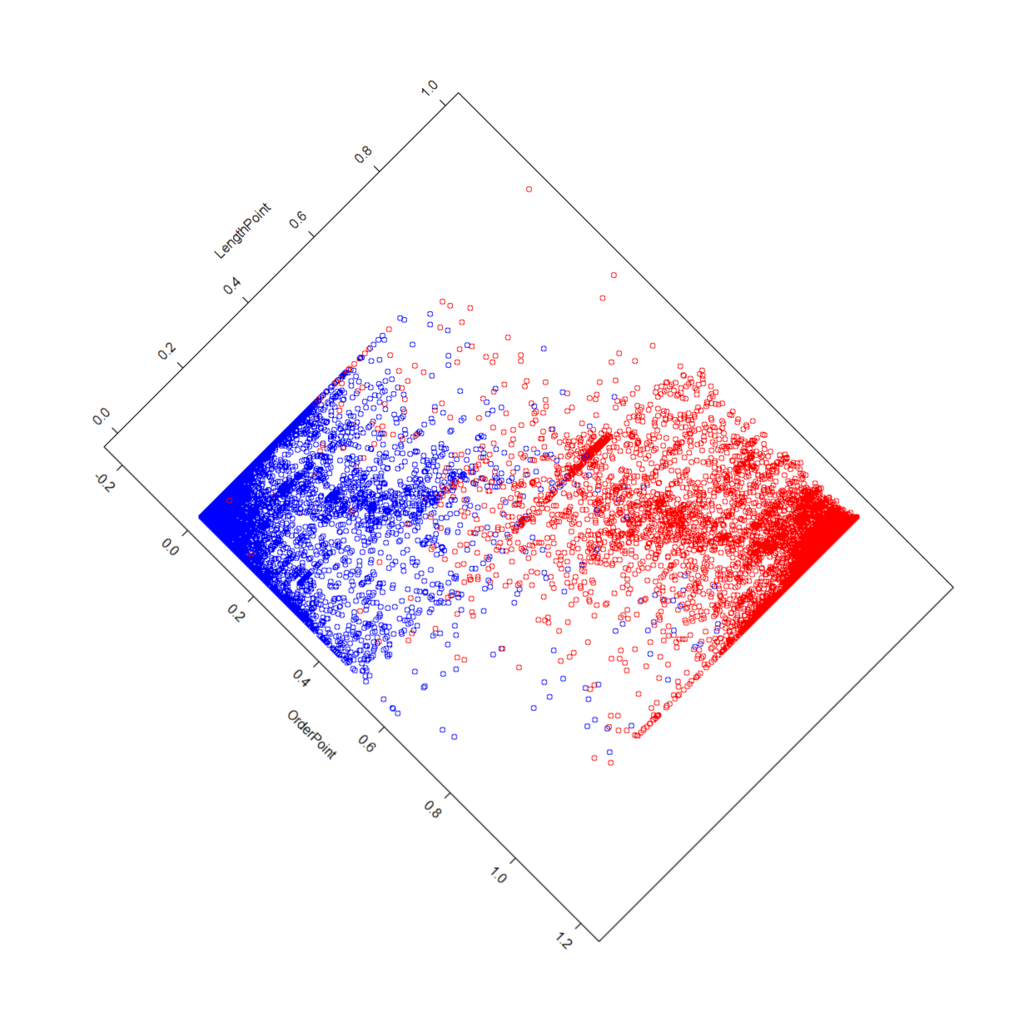
こんな感じ
prcompを使って主成分分析してみると...
PC1で全体の96.9%が説明できて、それは
OrderPoint*0.7071068 + LengthPoint *0.7071068(ぴったり45°回転!??!?)と言っています。
つまり、OrderPoint+LengthPointが一番大きいやつが正しい姓名分割ができてるやつだ、という計算をすればよいことになります。
なんか本当に合っているのか疑ってしまうくらいぴったりな結果が出てしまいました。
しかしながらこうすることによって式の正しさを保ちながら姓名分離することができるようになりましたとさ。
改めて制度検証
例のサッカー選手データ
前回 4人不正解/394人
今回 5人不正解/394人
今度解説するアイマスデータ
前回 3人不正解/174人
今回 4人不正解/174人
精度落ちとるやないか!
ということであわてて学習用人名を17000くらい追加したらサッカーデータ5人不正解、アイマスデータが2人不正解まで精度が上がりました。
まとめ
- 多重共線性っぽかったら、主成分分析をしましょう
- 計算バグがあって精度が高いよりバグがなくて精度が低いほうが気持ちいい